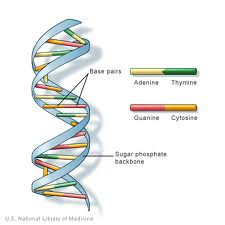
Il DNA (acido desossiribonucleico) è l’informazione genetica che si trova nei nuclei della maggior parte degli organismi. È organizzato in strutture chiamate cromosomi. La struttura del DNA è stata identificata per la prima volta come una struttura a “doppia elica” da Watson e Crick nel 1953. Il DNA è composto da 4 basi: le purine ,adenina (A) e guanina (G) e pirimidine, timina (T) e citosina (C). Questi formano coppie di basi complementari di A – T e G-C., Il DNA contiene anche un gruppo fosfato collegato a uno zucchero desossiribosio. Il gruppo fosfato è attaccato allo zucchero attraverso un legame fosfodiestere. Gli esseri umani hanno 99.5% somiglianze con altri esseri umani nel loro DNA.
Struttura del DNA
Il DNA (acido desossiribonucleico) è una catena di monomeri (unità ripetute) chiamati “nucleotidi”. Un nucleotide è costituito da: uno zucchero desossiribosio 2` (Un pentoso a cinque atomi di carbonio simile a quello dello zucchero ribosio trovato nell’RNA., La sua formula chimica è C5H10O4), un gruppo fosfato (che forma un legame fosfodiestere: collegamento 2 zuccheri desossiribosio insieme) e una base azotata (uno da A (Adenina), C ( citosina), G ( guanina) o T (timina), che forma una catena laterale ramificazione dal 1′ carbonio del 2` zucchero desossiribosio).
La regione del gruppo zucchero/fosfato di desossiribosio è considerata la “spina dorsale” dei filamenti di DNA a causa del suo scopo strutturale e la sequenza di basi porta le informazioni gentiche. Al fine di produrre una struttura del DNA a doppio filamento, le interazioni si verificano tra basi complementari., Le coppie di basi complementari nel DNA interagiscono tra loro tramite legami idrogeno: le interazioni A-T consistono in 2 legami idrogeno intermolecolari, mentre le interazioni G-C consistono in 3 legami idrogeno intermolecolari. Tra queste basi ci sono interazioni idrofobiche note come forze di van der Waal. Queste interazioni formano ponti tra due catene di DNA, creando così una struttura a forma di “scala” a doppio filamento. Ogni filamento funge da modello per l’altro nella replicazione del DNA., Il DNA è copiato in mRNA (RNA messaggero) che trasporta le informazioni dal filamento originale del modello del DNA per essere coinvolto nella sintesi proteica. Il processo di DNA che è copiato in mRNA è definito trascrizione. L’mRNA trascritto viene quindi tradotto in un polipeptide in un processo chiamato traduzione da tRNA.
Nella doppia elica del DNA i fili della spina dorsale sono più vicini su un lato dell’elica che sull’altro. Ciò porta alla formazione di solchi maggiori e minori., La scanalatura maggiore è molto più ampia della scanalatura minore e questo significa che specifiche interazioni DNA-proteine possono avvenire sulla scanalatura maggiore a causa della spina dorsale non essere nel modo. I nucleotidi specifici che si affacciano nel solco principale sono i gruppi N7 e C6 delle purine e i gruppi C4 e C5 delle pirimidine, che accettano ioni idrogeno dagli amminoacidi nella proteina per formare legami idrogeno.
A causa della doppia struttura elicoidale del DNA, le basi azotate si trovano all’interno della struttura, formando un interno idrofobo., La carica negativa dei gruppi fosfato conferisce alla spina dorsale zucchero-fosfato del DNA una carica negativa, che respinge i nucleofili, compresa l’acqua. Ciò rende il DNA meno vulnerabile all’attacco nucleofilo, quindi il DNA è considerato una molecola molto stabile. Il DNA è molto più stabile dell’RNA poiché l’RNA è solo a filamento singolo – le basi azotate sono lasciate esposte all’attacco dei nucleofili su un lato.
Nel 1953, nonostante molte altre teorie, James Watson e Francis Crick scoprirono che la vera struttura di una molecola di DNA a doppio filamento era una “doppia elica”., Questo è stato risolto come risultato di modelli “stick-and-ball” che hanno creato, insieme all’utilizzo del lavoro dei colleghi scienziati Rosalind Franklin e Maurice Wilkins sulla cristallografia a raggi X. Le fotografie di diffrazione a raggi X ottenute da fibre di DNA, mostravano una forma a X unica, che illustra una struttura elicoidale, sebbene indicassero una struttura ripetuta di 3,4 Å per giro dell’elica, ogni base viene ruotata di 36 gradi rispetto a quella successiva. Il diametro dell’elica è 23,7 Å., Hanno scoperto che la spina dorsale zucchero-fosfato era all’esterno e le basi sono posizionate all’interno dell’elica.
Le informazioni di cui sopra descrivevano la forma B del DNA. Il DNA si trova anche nelle forme A e Z. Quando il DNA diventa disidratato, si può osservare la forma A. È anche destrorso, ma ci sono 11 basi per turno e l’elica è più ampia. Il diametro è di 25,5 Å. Un’altra differenza è che l’inclinazione delle coppie di basi aumenta di 18o, a 19o dalla perpendicolare all’asse dell’elica.
La forma Z differisce molto di più in quanto è una doppia elica mancina., Questa forma è raramente vista senza l’aiuto di alte concentrazioni di sale. I legami sono zigzagati come i legami sono alternati anti e syn (mentre A – e B-forme sono solo anti). La forma a Z è più stretta, con un diametro di soli 18,4 Å, ma c’è un aumento di 3,8 Å per coppia di basi. Si pensa che le transizioni tra le forme B e Z del DNA possano essere coinvolte nella regolazione della regolazione genica.
Il B-DNA è più comunemente visto in tutte le forme di vita, tuttavia, le strutture A-elicoidali e Z-elicoidali coesistono nelle cellule; cioè, è molto comune osservare una molecola di B-DNA e Z-DNA, in una conferma prevalentemente B-DNA.
Il DNA del muntjac indiano che è un cervo asiatico ha la lunghezza più lunga (circa 3 miliardi di nucleotidi) tra tutte le molecole di DNA conosciute di altri organismi.
Il DNA è caricato negativamente a causa degli ioni fosfato caricati negativley nella spina dorsale zucchero-fosfato. Quindi può essere utilizzato per l’elettroforesi su gel per identificare diverse lunghezze di DNA., La carica negativa della spina dorsale, insieme ai gruppi OH sullo zucchero desossiribosio, significa che la spina dorsale è idrofila poiché l’acqua può formare legami idrogeno con essa. Il centro della molecola di DNA è idrofobo a causa della mancanza di carica nelle basi del DNA. L’interno esterno e idrofobo idrofilico della molecola di DNA significa che è solubile in acqua.
Replicazione
La natura a doppio filamento del DNA è importante per il metodo di replicazione semi-conservativa del DNA., In questo processo, l’enzima DNA elicasi svolge la doppia elica rompendo i legami idrogeno tra le basi complementari su ciascun filo rivelando i 2 fili separati. Su questi fili ci sono le basi rivelate, che attraggono basi complementari su nucleotidi liberi. I nucleotidi liberi sono uniti insieme da un enzima DNA polimerasi. Il trifosfato di desossiribonucleotide (dNTPs) viene aggiunto al gruppo idrossilico 3′ sul filo crescente attraverso il gruppo trifosfato 5′ sul dNTP in entrata in una reazione di esterificazione., L’unione dei nucleotidi forma un nuovo filamento di DNA che è identico all’altro doppio filamento di DNA, in quanto utilizza uno dei filamenti originali come modello per la replicazione. Ogni figlia doppio filamento di DNA è costituito da un filamento genitore e un filo di nuovo sythesised.
Anche se entrambi i trefoli nella molecola di DNA parentale vengono copiati per formare prodotti identici, i due trefoli vengono copiati in modo leggermente diverso l’uno dall’altro. Ciò è dovuto al fatto che il DNA è sempre sintetizzato in una direzione da 5′ a 3′., Il filo da 3′ a 5′, noto come il filo principale, viene copiato continuamente dalla DNA polimerasi. L’altro filo è chiamato il filo in ritardo, in quanto viene replicato più lentamente. Per replicare il filo in ritardo, i primer RNA sono posizionati su diversi punti lungo il filo in ritardo da un enzima chiamato primasi. Gli spazi vuoti sul filo in ritardo tra i primer RNA sono replicati dalla DNA polimerasi e i brevi frammenti di DNA replicato sono noti come frammenti di Okazaki. Tuttavia, al fine di completare la replicazione del filamento in ritardo, i primer a RNA devono essere sostituiti da sequenze di DNA., Un’altra DNA polimerasi rimuove i primer RNA e sintetizza frammenti di DNA per sostituirli. I frammenti di Okazaki e le sostituzioni di primer RNA non sono ancora uniti, quindi la DNA ligasi viene in un lega tutti i frammenti di DNA insieme.
La teoria della replicazione semi-conservativa è stata dimostrata corretta dall’esperimento Messelson-Stahl. In questo esperimento, E. coli sono stati coltivati in un mezzo contenente 15-N per un certo numero di generazioni. I batteri sono stati quindi trasferiti in un mezzo contenente 14-N. Dopo un ciclo di replicazione il DNA è stato estratto dai batteri e centrifugato., La centrifugazione separava il DNA per densità, producendo una densità di banda wita h tra quella del DNA 15-N e del DNA 14-N. Ciò ha mostrato che un filamento proveniva dal genitore (15-N) e un filamento è stato recentemente sintetizzato da nucleotidi liberi (14-N).