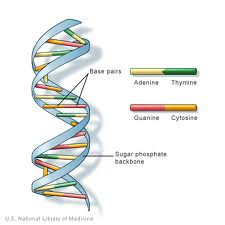
die DNA (Desoxyribonukleinsäure) ist das genetische Informationen finden sich in den Kernen der meisten Organismen. Es ist in Strukturen angeordnet, die Chromosomen genannt werden. Die Struktur der DNA wurde erstmals 1953 von Watson und Crick als „Doppelhelix“ -Struktur identifiziert. DNA besteht aus 4 Basen: die Purine, Adenin (A) und Guanin (G) und Pyrimidine ,Thymin (T) und Cytosin (C). Diese bilden komplementäre Basenpaare von A-T und G-C., DNA enthält auch eine Phosphatgruppe, die mit einem Desoxyribosezucker verbunden ist. Die Phosphatgruppe wird durch eine Phosphodiesterbindung an den Zucker gebunden. Menschen haben 99,5% Ähnlichkeiten mit anderen Menschen in ihrer DNA.
Struktur der DNA
DNA (Desoxyribonukleinsäure) ist eine Kette von Monomeren (sich wiederholende Einheiten), die als „Nukleotide“bezeichnet werden. Ein Nukleotid besteht aus: einem 2` Desoxyribose-Zucker (Eine Fünf-Kohlenstoff-Pentose ähnlich der von Ribose-Zucker in RNA gefunden., Seine chemische Formel ist C5H10O4), eine Phosphatgruppe (die eine Phosphodiesterbindung bildet: verbindet 2 Desoxyribosezucker miteinander) und eine stickstoffhaltige Base (eine aus A ( Adenin), C ( Cytosin), G (Guanin) oder T (Thymin), die eine Seitenkette bildet, die sich vom 1′ Kohlenstoff des 2` Desoxyribosezuckers verzweigt).
Die Desoxyribose-Zucker / Phosphat-Gruppenregion wird aufgrund ihres strukturellen Zwecks als „Rückgrat“ der DNA-Stränge angesehen, und die Basenfolge trägt die gentischen Informationen. Um eine doppelsträngige DNA-Struktur zu erzeugen, treten Wechselwirkungen zwischen komplementären Basen auf., Die komplementären Basenpaare in DNA interagieren über Wasserstoffbrücken miteinander: A-T-Wechselwirkungen bestehen aus 2 intermolekularen Wasserstoffbrücken, während G-C-Wechselwirkungen aus 3 intermolekularen Wasserstoffbrücken bestehen. Zwischen diesen Basen befinden sich hydrophobe Wechselwirkungen, die als Van-der-Waal-Kräfte bekannt sind. Diese Wechselwirkungen bilden Brücken zwischen zwei DNA-Ketten und bilden so eine doppelsträngige „Leiter“ -förmige Struktur. Jeder Strang fungiert als Vorlage für den anderen bei der DNA-Replikation., DNA wird in mRNA (Messenger RNA) kopiert, die die Informationen aus dem ursprünglichen DNA-Template-Strang trägt, um an der Proteinsynthese beteiligt zu sein. Der Prozess der DNA, die in mRNA kopiert wird, wird als Transkription bezeichnet. Die transkribierte mRNA wird dann in einem Prozess, der Translation by tRNA genannt wird, in ein Polypeptid übersetzt.
In der DNA-Doppelhelix sind die Stränge des Rückgrats auf einer Seite der Helix näher zusammen als auf der anderen. Dies führt zur Bildung von Dur-und Moll-Rillen., Die Hauptrille ist viel breiter als die Nebenrille und dies bedeutet, dass spezifische DNA-Protein-Wechselwirkungen auf der Hauptrille stattfinden können, da das Rückgrat nicht im Weg ist. Die spezifischen Nukleotide, die in die Hauptnut eingeführt werden, sind die N7-und C6-Puringruppen und die C4-und C5-Pyrimidingruppen, die Wasserstoffionen aus den Aminosäuren im Protein zur Bildung von Wasserstoffbrücken akzeptieren.
Aufgrund der doppelhelikalen Struktur der DNA befinden sich die stickstoffhaltigen Basen an der Innenseite der Struktur und bilden ein hydrophobes Innere., Die negative Ladung aus den Phosphatgruppen gibt dem Zucker-Phosphat-Rückgrat der DNA eine negative Ladung, die Nukleophile, einschließlich Wasser, abstößt. Dies macht DNA weniger anfällig für nukleophile Angriffe, daher wird DNA als ein sehr stabiles Molekül angesehen. DNA ist viel stabiler als RNA, da RNA nur einzelsträngig ist – die stickstoffhaltigen Basen sind auf einer Seite dem Angriff von Nukleophilen ausgesetzt.
Trotz vieler anderer Theorien entdeckten James Watson und Francis Crick 1953 die wahre Struktur eines doppelsträngigen DNA-Moleküls als „Doppelhelix“., Dies wurde als Ergebnis von „Stick-and-Ball“ – Modellen gelöst, die sie erstellt haben, zusammen mit der Arbeit der Kollegen Rosalind Franklin und Maurice Wilkins auf Röntgenkristallographie. Die Röntgenbeugungsfotos, die aus DNA-Fasern erhalten wurden, zeigten eine einzigartige Röntgenform, die eine spiralförmige Struktur veranschaulicht, obwohl sie eine sich wiederholende Struktur von 3,4 Å pro Umdrehung der Helix anzeigten, wobei jede Basis um 36 Grad von der nächsten gedreht wird. Der Durchmesser der Helix beträgt 23,7 Å., Sie fanden heraus, dass das Zuckerphosphat-Rückgrat außen war und die Basen auf der Innenseite der Helix positioniert sind.
Die obigen Informationen beschrieben die B-Form der DNA. DNA findet sich auch in A – und Z-Formen. Wenn die DNA dehydriert wird, kann die A-Form beobachtet werden. Es ist auch Rechtshänder, aber es gibt 11 Basen pro Runde und die Helix ist breiter. Der Durchmesser beträgt 25,5 Å. Ein weiterer Unterschied besteht darin, dass die Neigung der Basispaare von senkrecht zur Helix-Achse um 18o auf 19o zunimmt.
Die Z-Form unterscheidet sich wesentlich mehr, da es sich um eine linkshändige Doppelhelix handelt., Diese Form wird selten ohne die Hilfe hoher Salzkonzentrationen gesehen. Die Bindungen sind im Zickzack, da die Bindungen abwechselnd anti und syn sind (während A – und B-Formen nur anti sind). Die Z-Form ist schmaler und hat einen Durchmesser von nur 18,4 Å, aber es gibt einen Anstieg von 3,8 Å pro Basispaar. Es wird angenommen, dass Übergänge zwischen den B-und Z-Formen von DNA an der Regulation der Genregulation beteiligt sein können. B-DNA wird am häufigsten in allen Lebensformen gesehen, jedoch koexistieren A-helikale und Z-helikale Strukturen in Zellen; d.h., es ist sehr üblich , ein Molekül von B-DNA und Z-DNA in einer überwiegend B-DNA-Bestätigung zu beobachten.
Die DNA des indischen Muntjac, eines asiatischen Hirsches, hat unter allen bekannten DNA-Molekülen anderer Organismen die längste Länge (ungefähr 3 Milliarden Nukleotide).
Die DNA ist aufgrund der negativ geladenen Phosphationen im Zucker-Phosphat-Rückgrat negativ geladen. Daher kann es für die Gelelektrophorese verwendet werden, um verschiedene DNA-Längen zu identifizieren., Die negative Ladung des Rückgrats, zusammen mit den OH-Gruppen auf dem Desoxyribose-Zucker, bedeutet, dass das Rückgrat hydrophil ist, da Wasser Wasserstoffbindungen mit ihm bilden kann. Das Zentrum des DNA-Moleküls ist aufgrund der fehlenden Ladung in DNA-Basen hydrophob. Das hydrophobe Äußere und hydrophobe Innere des DNA-Moleküls bedeutet, dass es in Wasser löslich ist.
Replikation
Die doppelsträngige Natur der DNA ist wichtig für die „semi-konservative Replikationsmethode“ der DNA-Replikation., Bei diesem Prozess wickelt das Enzym DNA Helicase die Doppelhelix ab, indem es die Wasserstoffbrücken zwischen den komplementären Basen an jedem Strang aufbricht und die 2 separaten Stränge enthüllt. Auf diesen Strängen befinden sich die offenbarten Basen, die komplementäre Basen auf freien Nukleotiden anziehen. Die freien Nukleotide werden durch ein Enzym DNA-Polymerase miteinander verbunden. Desoxyribonukleotidtriphosphat (dNTPs) werden auf die 3′ Hydroxylgruppe auf dem wachsenden Strang durch die 5′ Triphosphatgruppe auf dem ankommenden dNTP in einer Veresterungsreaktion hinzugefügt., Die Verbindung von Nukleotiden bildet einen neuen DNA-Strang, der mit dem anderen Doppelstrang der DNA identisch ist, da er einen der ursprünglichen Stränge als Vorlage für die Replikation verwendet. Jeder Tochterdoppelstrang der DNA besteht aus einem Elternstrang und einem neu sythesisierten Strang.
Obwohl beide Stränge im elterlichen DNA-Molekül kopiert werden, um identische Produkte zu bilden, werden die beiden Stränge auf eine etwas andere Weise voneinander kopiert. Dies liegt daran, dass DNA immer in 5′ bis 3′ Richtung synthetisiert wird., Der 3′ bis 5 ‚ – Strang, der als führender Strang bekannt ist, wird kontinuierlich durch DNA-Polymerase kopiert. Der andere Strang wird als verzögerter Strang bezeichnet, da er langsamer repliziert wird. Um den verzögerten Strang zu replizieren, werden RNA-Primer an mehreren Punkten entlang des verzögerten Strangs durch ein Enzym namens Primase platziert. Die Lücken auf dem verzögerten Strang zwischen den RNA-Primern werden durch DNA-Polymerase repliziert, und die kurzen Fragmente der replizierten DNA werden als Okazaki-Fragmente bezeichnet. Um die Replikation des verzögerten Strangs abzuschließen, müssen RNA-Primer jedoch durch DNA-Sequenzen ersetzt werden., Eine andere DNA-Polymerase entfernt die RNA-Primer und synthetisiert DNA-Fragmente, um sie zu ersetzen. Die Okazaki-Fragmente und der RNA-Primer-Ersatz sind immer noch nicht verbunden, so DNA-Ligase kommt in einem ligiert alle Fragmente der DNA zusammen.
Die Theorie der halbkonservativen Replikation hat sich im Messelson-Stahl-Experiment als richtig erwiesen. In diesem Experiment wurden E. coli in einem Medium mit 15-N für eine Reihe von Generationen gezüchtet. Die Bakterien wurden dann auf ein Medium übertragen, das 14-N enthielt. Nach einem Replikationszyklus wurde DNA aus den Bakterien extrahiert und zentrifugiert., Die Zentrifugation trennte die DNA nach Dichte und erzeugte eine Band wita h Dichte zwischen der von 15-N-DNA und 14-N-DNA. Dies zeigte, dass ein Strang vom Elternteil (15-N) stammte und ein Strang neu aus freien Nukleotiden (14-N) synthetisiert wurde.