przegląd
16S rRNA oznacza 16S kwas rybosomalny rybonukleinowy (rRNA), gdzie S (Svedberg) jest jednostką miary (szybkość sedymentacji). RRNA jest ważnym składnikiem małej podjednostki (SSU) prokariotycznych rybosomów, a także mitochondriów i chloroplastów. Rysunek 1 pokazuje, jak 16S rRNA (krótko 16S) bierze udział w prokariotycznym rybosomie.
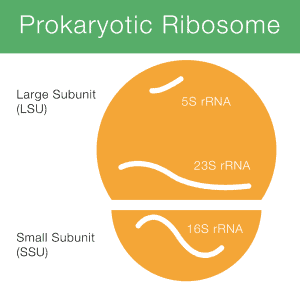
kodowanie DNAsegment dla rRNA nazywa się genem rRNA lub rDNA., Do celów sekwencjonowania, informacja o sekwencji jest uzyskiwana z genu 16S, ponieważ DNA jest znacznie łatwiejsze do przetworzenia i sekwencji niż RNA.
dlaczego 16S rRNA został wybrany jako cząsteczka kodu kreskowego DNA dla taksonomii i ekologii
- aby być używanym jako kod kreskowy DNA, Gen powinien mieć następujące cechy.
powinien być wszechobecny. W przeciwnym razie nie możemy uwzględnić wszystkich organizmów. Wszyscy członkowie bakterii i Archeea są znani z genu 16S. - powinien zawierać wystarczającą ilość informacji filogenetycznych. 16S ma długość około 1500 bp, co nie jest zbyt krótkie ani długie.,
- zmienność genetyczna w obrębie genu 16S występującego wśród prokariotów jest odpowiednia do wykorzystania w analizie filogenetycznej dla szerokich zakresów taksonomicznych. Jest on z powodzeniem stosowany do wnioskowania o pokrewieństwie filogenetycznym między phyllami, a także stosowany w porównywaniu gatunków z tego samego rodzaju.
- powinien być łatwo wzmacniany przez PCR. Gen 16S ma wiele zachowanych regionów, które mogą być używane jako miejsca gruntowania. Staje się to znaczącą zaletą dla sekwencjonowania krótkiego odczytu opartego na NGS.,
- Po wielu latach międzynarodowej współpracy mamy bazę sekwencji 16S zawierającą prawie wszystkie znane gatunki bakterii i archeonów. Przeszukując sekwencję 16S w tych bazach danych, każdy, nawet bez znajomości poważnej taksonomii, może zidentyfikować nowo wyizolowane szczepy.
zmienne regiony 16S i primery PCR w celu ich wzmocnienia
zmienność sekwencji wśród bakteryjnych 16S jest znana z tego, że nie są równomiernie rozłożone. Wśród bakterii zidentyfikowano dziewięć hiperwariowalnych regionów, które noszą nazwy od V1 do V9.,TTCCTTTRAGTTT
The full-length 16S gene is usually amplified by the pair of primers 27F and 1492R, followed by Sanger DNA sequencing., Aby uzyskać dokładną sekwencję, obie nici DNA należy zsekwencjonować za pomocą wielu primerów podanych w powyższej tabeli.
zastosowanie NGS do analizy społeczności bakterii
NGS jest właściwe dla wyjaśnienia struktury społeczności bakterii, ponieważ eliminuje wymóg żmudnego klonowania E. coli i umożliwia sekwencjonowanie DNA o wysokiej przepustowości. Ponieważ różne długości DNA są sekwencjonowane przez różne platformy NGS, należy użyć odpowiedniej pary primerów PCR., Możliwe są trzy rodzaje sekwencjonowania NGS:
- sekwencjonowanie jednokrotne: informacja o sekwencji DNA jest uzyskiwana tylko z jednego końca amplikonu PCR. Roche 454, torrenty jonowe
- sekwencjonowanie w parach: informacja o sekwencji DNA jest uzyskiwana z obu końców amplikonu PCR. Dwie sekwencje powinny być nakładane na siebie przez wystarczającą długość sieci, aby połączyć się, aby stać się pojedynczą sekwencją. Illumina
- Circular consensus sequencing (cca): Technologia Smrt Pacific Biosciences zapewnia bardzo długie odczyty pojedynczej cząsteczki w zakresie>10K bp., Ze względu na zastosowaną bibliotekę o okrągłym kształcie, ten sam amplikon 16S może być sekwencjonowany wielokrotnie, aby uzyskać dokładną sekwencję konsensusu.