overzicht
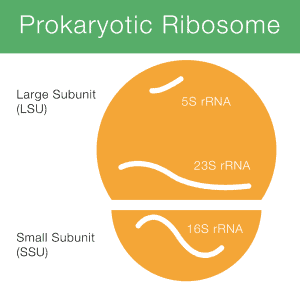
16S rRNA staat voor 16S ribosomaal ribonucleïnezuur (rRNA), waarbij S (Svedberg) een meeteenheid is (sedimentatiesnelheid). Dit rRNA is een belangrijk bestanddeel van de kleine subeenheid (SSU) van prokaryotic ribosomen evenals mitochondria en chloroplasten. Figuur 1 toont hoe 16S rRNA (kort 16S) betrokken is bij een prokaryotic ribosoom.
DNAsegment codering voor rRNA wordt rRNA gen of rDNA genoemd., Voor het rangschikken, wordt de opeenvolgingsinformatie verkregen van het 16S gen omdat DNA veel gemakkelijker te verwerken en opeenvolging dan RNA is.
waarom 16S rRNA werd gekozen als DNA-barcodemolecuul voor taxonomie en ecologie
- om als DNA-barcode te worden gebruikt, moet een gen de volgende kenmerken hebben.
Het moet alom aanwezig zijn. Anders kunnen we niet alle organismen erbij betrekken. Van alle leden van bacteriën en Archaea is bekend dat ze 16S-gen hebben. - Het moet voldoende fylogenetische informatie bevatten. 16S is ongeveer 1500 bp lang, wat niet te kort of lang is.,
- de genetische variatie binnen 16S gen gevonden onder prokaryoten is voldoende om te worden gebruikt in de fylogenetische analyse voor de brede taxonomische bereiken. Het wordt met succes gebruikt om phylogenetic verhouding onder phyla af te leiden terwijl ook in de vergelijking onder species in het zelfde geslacht wordt gebruikt.
- Het moet gemakkelijk worden versterkt door PCR. 16S gen heeft veelvoudige behouden gebieden die als het priming plaatsen kunnen worden gebruikt. Dit wordt een significant voordeel voor het op NGS-gebaseerde korte lezen rangschikken.,
- na vele jaren van internationale samenwerking hebben we een 16S sequentiedatabase met bijna alle bekende bacteriesoorten en Archaea. Door 16S sequentie te doorzoeken met deze databases, kan iedereen, zelfs zonder kennis van ernstige taxonomie, nieuw geïsoleerde stammen identificeren.
Variable regions of 16S and PCR primers to amplify them
Sequence variation between bacterial 16S is known to be not uniformly distributed. Negen hypervariable gebieden werden geà dentificeerd onder bacteriën, die v1 aan V9 worden genoemd.,TTCCTTTRAGTTT
The full-length 16S gene is usually amplified by the pair of primers 27F and 1492R, followed by Sanger DNA sequencing., Om nauwkeurige opeenvolging te verkrijgen, zouden beide bundels van DNA moeten worden gerangschikt gebruikend veelvoudige inleidingen die in de bovenstaande lijst worden gegeven.
toepassing van NGS op bacteriële gemeenschapsanalyse
NGS is juist om de structuur van de bacteriële gemeenschap te verduidelijken, aangezien het de eis van vervelend E. coli klonen elimineert en een hoge productie DNA sequencing mogelijk maakt. Omdat de verschillende lengtes van DNA door diverse platforms van NGS worden gerangschikt, zou een geschikt paar PCR-inleidingen moeten worden gebruikt., Er zijn drie soorten NGS-sequencing mogelijk:
- single-end sequencing: DNA-sequentiegegevens worden verkregen uit slechts één uiteinde van het PCR-amplicon. Roche 454, Ionentorrents
- gepaarde eindsequentiebepaling: informatie over de DNA-sequentie wordt verkregen aan beide uiteinden van het PCR-amplicon. Twee opeenvolgingen zouden door een sufficnetlengte moeten worden overlapt te combineren om één enkele opeenvolging te worden. Illumina
- Circular consensus sequencing (CCA): de Smrt-technologie van Pacific Biosciences biedt zeer lange enkelvoudige molecuullezingen variërend van >10K bp., Vanwege de gebruikte cirkelvormige bibliotheek, kan dezelfde 16S amplicon meerdere keren worden gesequenced om nauwkeurige consensusvolgorde te produceren.