Panoramica
16S rRNA è l’acronimo di 16S ribosomal ribonucleic acid (rRNA), dove S (Svedberg) è un’unità di misura (velocità di sedimentazione). Questo rRNA è un costituente importante della piccola subunità (SSU) dei ribosomi procarioti, dei mitocondri e dei cloroplasti. Figura 1 mostra come il 16S rRNA (poco 16S) è coinvolto in un ribosoma procariotico.
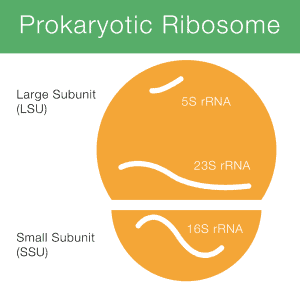
La codifica DNAsegment per rRNA è chiamata gene rRNA o rDNA., Ai fini del sequenziamento, le informazioni sulla sequenza sono ottenute dal gene 16S perché il DNA è molto più facile da elaborare e sequenziare rispetto all’RNA.
Perché 16S rRNA è stato scelto come molecola del codice a barre del DNA per la tassonomia e l’ecologia
- Per essere usato come codice a barre del DNA, un gene dovrebbe avere le seguenti caratteristiche.
Dovrebbe essere presente ovunque. Altrimenti, non possiamo includere tutti gli organismi. Tutti i membri di batteri e Archaea sono noti per avere gene 16S. - Dovrebbe contenere sufficienti informazioni filogenetiche. 16S è lungo circa 1.500 bp, che non è troppo corto o lungo.,
- La variazione genetica all’interno del gene 16S trovato tra i procarioti è adeguata per essere utilizzata nell’analisi filogenetica per le ampie gamme tassonomiche. È usato con successo per dedurre la relazione filogenetica fra phyla mentre anche usato nel confronto fra le specie nello stesso genere.
- Dovrebbe essere facilmente amplificato da PCR. Il gene 16S ha più regioni conservate che possono essere utilizzate come siti di priming. Questo diventa un vantaggio significativo per il sequenziamento di lettura breve basato su NGS.,
- Dopo molti anni di collaborazione internazionale, abbiamo un database di sequenze 16S che contiene quasi tutte le specie conosciute di batteri e Archaea. Cercando la sequenza 16S contro questi database, chiunque, anche senza la conoscenza della tassonomia seria, può identificare i ceppi recentemente isolati.
Regioni variabili di 16S e primer PCR per amplificarle
La variazione di sequenza tra 16S batterici è nota per non essere distribuita uniformemente. Nove regioni ipervariabili sono state identificate tra i batteri, che sono denominati da V1 a V9.,TTCCTTTRAGTTT
The full-length 16S gene is usually amplified by the pair of primers 27F and 1492R, followed by Sanger DNA sequencing., Per ottenere una sequenza accurata, entrambi i filamenti di DNA devono essere sequenziati utilizzando più primer indicati nella tabella precedente.
Applicazione di NGS all’analisi della comunità batterica
NGS è giusto per chiarire la struttura della comunità batterica, in quanto elimina il requisito della noiosa clonazione di E. coli e consente un sequenziamento del DNA ad alta velocità. Poiché diverse lunghezze di DNA sono sequenziate da varie piattaforme NGS, è necessario utilizzare una coppia adatta di primer PCR., Sono possibili tre tipi di sequenziamento NGS:
- Sequenziamento single-end: le informazioni sulla sequenza del DNA sono ottenute da una sola estremità dell’amplicone PCR. Roche 454, Ion Torrents
- Paired-end sequencing: le informazioni sulla sequenza del DNA sono ottenute da entrambe le estremità dell’amplicone PCR. Due sequenze dovrebbero essere sovrapposte da una lunghezza sufficnet da combinare per diventare una singola sequenza. Illumina
- Circular consensus sequencing (cca): la tecnologia SMRT di Pacific Biosciences fornisce letture a singola molecola molto lunghe che vanno>10K bp., A causa della libreria a forma circolare utilizzata, lo stesso amplicone 16S può essere sequenziato più volte per produrre una sequenza di consenso accurata.