Aperçu
16S ARNr signifie acide ribosomique ribonucléique 16S (ARNr), où S (Svedberg) est une unité de mesure (vitesse de sédimentation). Cet ARNr est un constituant important de la petite sous-unité (SSU) des ribosomes procaryotes ainsi que des mitochondries et des chloroplastes. La figure 1 montre comment l’ARNr 16S (bientôt 16S) est impliqué dans un ribosome procaryote.
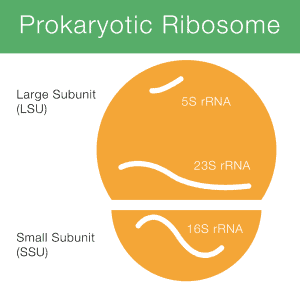
Le codage de l’ADN pour l’ARNr est appelé gène de l’ARNr ou ADNr., Aux fins du séquençage, les informations de séquence sont obtenues à partir du gène 16S car l’ADN est beaucoup plus facile à traiter et à séquencer que l’ARN.
Pourquoi l’ARNr 16S a été choisi comme molécule de code-barres d’ADN pour la taxonomie et l’écologie
- Pour être utilisé comme code-barres d’ADN, un gène devrait avoir les caractéristiques suivantes.
Il devrait être omniprésents. Sinon, nous ne pouvons pas inclure tous les organismes. Tous les membres des bactéries et des Archées sont connus pour avoir le gène 16S. - Il doit contenir suffisamment d’informations phylogénétiques. 16S est d’environ 1 500 bp de long, ce qui n’est ni trop court ni trop long.,
- La variation génétique au sein du gène 16S trouvé chez les procaryotes est adéquate pour être utilisée dans l’analyse phylogénétique pour les grandes gammes taxonomiques. Il est utilisé avec succès pour inférer la relation phylogénétique entre phyla tout en étant également utilisé dans la comparaison entre les espèces du même genre.
- Il devrait être facilement amplifié par PCR. Le gène 16S a plusieurs régions conservées qui peuvent être utilisées comme sites d’amorçage. Cela devient un avantage important pour le séquençage de lecture courte basé sur NGS.,
- Après de nombreuses années de collaboration internationale, nous avons une base de données de séquences 16S contenant presque toutes les espèces connues de bactéries et d’Archées. En recherchant la séquence 16S dans ces bases de données, n’importe qui, même sans connaissance de la taxonomie sérieuse, peut identifier des souches nouvellement isolées.
Régions variables de 16S et amorces de PCR pour les amplifier
La variation de séquence parmi les 16S bactériens n’est pas uniformément distribuée. Neuf régions hypervariables ont été identifiées parmi les bactéries, qui sont nommées V1 à V9.,TTCCTTTRAGTTT
The full-length 16S gene is usually amplified by the pair of primers 27F and 1492R, followed by Sanger DNA sequencing., Pour obtenir une séquence précise, les deux brins d’ADN doivent être séquencés à l’aide de plusieurs amorces données dans le tableau ci-dessus.
Application de NGS à l’analyse de la communauté bactérienne
NGS est bon pour élucider la structure de la communauté bactérienne, car il élimine l’exigence de clonage fastidieux d’E. coli et permet un séquençage de l’ADN à haut débit. Étant donné que différentes longueurs d’ADN sont séquencées par différentes plates-formes NGS, une paire appropriée d’amorces PCR doit être utilisée., Trois types de séquençage NGS sont possibles:
- Séquençage à une extrémité: les informations de séquence d’ADN sont obtenues à partir d’une seule extrémité de l’amplicon PCR. Roche 454, Ion Torrents
- Séquençage par paires: Les informations de séquence d’ADN sont obtenues à partir des deux extrémités de l’amplicon de PCR. Deux séquences doivent être superposées par une longueur sufficnet pour se combiner pour devenir une seule séquence. Illumina
- Circular consensus sequencing (cca): La technologie SMRT de Pacific Biosciences fournit de très longues lectures de molécules uniques allant>10K bp., En raison de la bibliothèque de forme circulaire utilisée, le même amplicon 16S peut être séquencé plusieurs fois pour produire une séquence de consensus précise.