resumen
16S rRNA significa ácido ribonucleico ribosomal 16S (rRNA), donde S (Svedberg) es una unidad de medida (velocidad de sedimentación). Este ARNr es un componente importante de la subunidad pequeña (SSU) de los ribosomas procarióticos, así como de las mitocondrias y cloroplastos. La figura 1 muestra cómo el ARNr 16S (en breve 16S) está involucrado en un ribosoma procariótico.
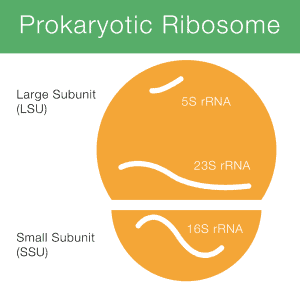
la codificación del DNAsegment para rRNA se llama gen rRNA o rDNA., Para los propósitos de secuenciación, la información de secuencia se obtiene del gen 16S porque el ADN es mucho más fácil de procesar y secuenciar que el ARN.
por qué 16S rRNA fue elegido como molécula de código de barras de ADN para Taxonomía y ecología
- para ser utilizado como un código de barras de ADN, un gen debe tener las siguientes características.debe estar omnipresente. De lo contrario, no podemos incluir a todos los organismos. Se sabe que todos los miembros de las bacterias y arqueas tienen el gen 16S.
- debe contener suficiente información filogenética. 16S es de aproximadamente 1,500 bp de largo, que no es demasiado corto o largo.,
- la variación genética dentro del gen 16S encontrada entre procariotas es adecuada para ser utilizada en el análisis filogenético para los amplios rangos taxonómicos. Se utiliza con éxito para inferir la relación filogenética entre los filos, mientras que también se utiliza en la comparación entre especies del mismo género.
- Debe ser fácilmente amplificado por PCR. El gen 16S tiene múltiples regiones conservadas que se pueden usar como sitios de cebado. Esto se convierte en una ventaja significativa para la secuenciación de lectura corta basada en NGS.,
- después de muchos años de colaboración internacional, tenemos una base de datos de secuencias 16S que contiene casi todas las especies conocidas de bacterias y arqueas. Al buscar la secuencia 16S en estas bases de datos, cualquiera, incluso sin conocimiento de una taxonomía seria, puede identificar cepas recién aisladas.
las regiones variables de 16S y los cebadores de PCR para amplificarlos
se sabe que la variación de secuencia entre 16S bacterianos no está distribuida uniformemente. Se identificaron nueve regiones hipervariables entre las bacterias, que se denominan V1 a V9.,TTCCTTTRAGTTT
The full-length 16S gene is usually amplified by the pair of primers 27F and 1492R, followed by Sanger DNA sequencing., Para obtener una secuencia precisa, ambas hebras de ADN deben secuenciarse utilizando múltiples cebadores indicados en la tabla anterior.
La aplicación de NGS al análisis de la comunidad bacteriana
NGS es adecuada para dilucidar la estructura de la comunidad bacteriana, ya que elimina el requisito de la tediosa clonación de E. coli y permite la secuenciación de ADN de alto rendimiento. Debido a que diferentes longitudes de ADN son secuenciadas por varias plataformas NGS, se debe usar un par adecuado de cebadores PCR., Tres tipos de secuenciación NGS son posibles:
- secuenciación de un solo extremo: la información de la secuencia de ADN se obtiene de un solo extremo del amplicón PCR. Roche 454, Ion Torrents
- secuenciación de extremos emparejados: la información de la secuencia de ADN se obtiene de ambos extremos del amplicón PCR. Dos secuencias deben superponerse con una longitud sufficnet para combinarse y convertirse en una sola secuencia. Illumina
- secuenciación de consenso Circular (cca): la tecnología SMRT de Pacific Biosciences proporciona lecturas muy largas de una sola molécula que van > 10k bp., Debido a la biblioteca de forma circular utilizada, el mismo amplicón 16S se puede secuenciar varias veces para producir una secuencia de consenso precisa.