Oversigt
16S rRNA ‘ et står for 16S ribosom ribonukleinsyre (rRNA), hvor S (Svedberg) er en måleenhed (sænkningsreaktion). Denne rRNA er en vigtig bestanddel af den lille underenhed (SSU) af prokaryote ribosomer såvel som mitokondrier og chloroplaster. Figur 1 viser, hvordan 16S rRNA (kort 16S) er involveret i et prokaryotisk ribosom.
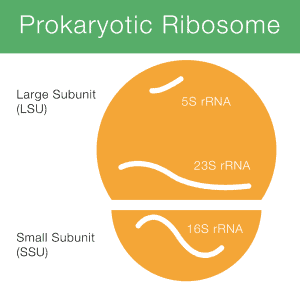
DNAsegment kodning for rRNA kaldes enten rRNA gen eller rDNA., Med henblik på sekventering opnås sekvensinformation fra 16S-genet, fordi DNA er meget lettere at behandle og sekvensere end RNA.
hvorfor 16S rRNA blev valgt som DNA-stregkodemolekyle til taksonomi og økologi
- for at blive brugt som en DNA-stregkode skal et gen have følgende egenskaber.
det skal være allestedsnærværende til stede. Ellers kan vi ikke inkludere alle organismer. Alle medlemmer af bakterier og Archaea er kendt for at have 16S gen. - det skal indeholde tilstrækkelig fylogenetisk information. 16S er omkring 1.500 bp lang, hvilket ikke er for kort eller langt.,
- den genetiske variation inden for 16S-genet, der findes blandt prokaryoter, er tilstrækkelig til at blive anvendt i den fylogenetiske analyse for de brede taksonomiske intervaller. Det bruges med succes til at udlede fylogenetisk forhold mellem phyla, mens det også bruges til sammenligning mellem arter i samme slægt.
- det bør let forstærkes ved PCR. 16S gen har flere bevarede regioner, der kan bruges som priming sites. Dette bliver en betydelig fordel for NGS-baserede korte læse sekventering.,
- efter mange års internationalt samarbejde, har vi 16 sekvens database holder næsten alle kendte arter af bakterier og arkæa. Ved at søge 16S sekvens mod disse databaser, nogen, selv uden kendskab til alvorlige taksonomi, kan identificere nyligt isolerede stammer.
Variable regioner på 16 ‘ere og PCR-primere for at forstærke dem
Sekvensvariation blandt bakterielle 16′ ere vides ikke at være ensartet fordelt. Ni hypervariable regioner blev identificeret blandt bakterier, der hedder V1 til v9.,TTCCTTTRAGTTT
The full-length 16S gene is usually amplified by the pair of primers 27F and 1492R, followed by Sanger DNA sequencing., For at opnå nøjagtig sekvens skal begge DNA-strenge sekventeres ved hjælp af flere primere angivet i ovenstående tabel.
Anvendelse af NGS til bakterielle samfund analyse
NGS er det rigtige for proteinernes bakteriel fællesskabets struktur, da det fjerner kravet om kedelig E. coli kloning og giver high throughput DNA-sekventering. Da forskellige længder af DNA sekventeres af forskellige NGS-platforme, bør der anvendes et passende par PCR-primere., Tre typer NGS-sekventering er mulige:
- Single-end-sekventering: DNA-sekvensinformation opnås fra kun den ene ende af PCR-ampliconen. Roche 454, Iontorrenter
- parret sekventering: DNA-sekvensinformation opnås fra begge ender af PCR-ampliconen. To sekvenser skal overlappes af en tilstrækkelig længde til at kombinere for at blive en enkelt sekvens. Illumina
- Cirkulære konsensus-sekventering (cca): Pacific Biosciences’ SMQYART teknologi giver meget lang enkelt molekyle læser lige >10K bp., På grund af den cirkulære-formet bibliotek anvendes, den samme 16S amplicon kan sekventeres flere gange for at producere nøjagtige konsensus sekvens.