Übersicht
16S rRNA steht für 16S ribosomale Ribonukleinsäure (rRNA), wobei S (Svedberg) eine Maßeinheit (Sedimentationsrate) ist. Diese rRNA ist ein wichtiger Bestandteil der Small Subunit (SSU) prokaryotischer Ribosomen sowie Mitochondrien und Chloroplasten. Abbildung 1 zeigt, wie die 16S-rRNA (kurz 16S) an einem prokaryotischen Ribosom beteiligt ist.
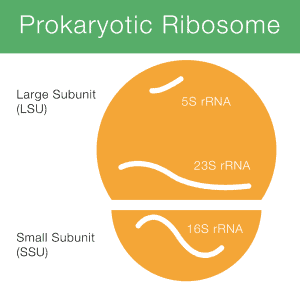
DNAsegment-Kodierung für rRNA wird entweder rRNA-Gen oder rDNA genannt., Für die Zwecke der Sequenzierung werden Sequenzinformationen aus dem 16S-Gen erhalten, da DNA viel einfacher zu verarbeiten und zu sequenzieren ist als RNA.
Warum 16S rRNA als DNA-Barcode-Molekül für Taxonomie und Ökologie ausgewählt wurde
- Um als DNA-Barcode verwendet zu werden, sollte ein Gen die folgenden Eigenschaften aufweisen.
Es sollte allgegenwärtig sein. Andernfalls können wir nicht alle Organismen einbeziehen. Es ist bekannt, dass alle Mitglieder von Bakterien und Archaeen ein 16S-Gen haben. - Es sollte genügend phylogenetische Informationen enthalten. 16S ist ungefähr 1,500 bp lang, was nicht zu kurz oder lang ist.,
- Die genetische Variation innerhalb des 16S-Gens, die bei Prokaryoten gefunden wird, ist ausreichend, um in der phylogenetischen Analyse für die breiten taxonomischen Bereiche verwendet zu werden. Es wird erfolgreich verwendet, um die phylogenetische Beziehung zwischen Phyla abzuleiten, während es auch beim Vergleich zwischen Arten derselben Gattung verwendet wird.
- Es sollte leicht durch PCR verstärkt werden. 16S-Gen hat mehrere konservierte Regionen, die als die Grundierungsstellen verwendet werden können. Dies wird zu einem signifikanten Vorteil für die NGS-basierte Kurzlesesequenzierung.,
- Nach langjähriger internationaler Zusammenarbeit verfügen wir über eine 16S-Sequenzdatenbank mit fast allen bekannten Bakterienarten und Archaeen. Durch die Suche nach 16S-Sequenzen anhand dieser Datenbanken kann jeder, auch ohne Kenntnis einer ernsthaften Taxonomie, neu isolierte Stämme identifizieren.
Variable Regionen von 16S und PCR-Primern, um sie zu amplifizieren
Es ist bekannt, dass die Sequenzvariation zwischen bakteriellen 16S nicht gleichmäßig verteilt ist. Neun hypervariable Regionen wurden unter Bakterien identifiziert, die V1 bis V9 heißen.,TTCCTTTRAGTTT
The full-length 16S gene is usually amplified by the pair of primers 27F and 1492R, followed by Sanger DNA sequencing., Um eine genaue Sequenz zu erhalten, sollten beide DNA-Stränge unter Verwendung mehrerer Primer sequenziert werden, die in der obigen Tabelle angegeben sind.
Anwendung von NGS auf bakterielle Community-Analyse
NGS ist das Richtige für die Aufklärung der bakteriellen Community-Struktur, da es die Anforderung eines langwierigen E. coli-Klonens eliminiert und eine DNA-Sequenzierung mit hohem Durchsatz ermöglicht. Da verschiedene DNA-Längen von verschiedenen NGS-Plattformen sequenziert werden, sollte ein geeignetes Paar PCR-Primer verwendet werden., Drei Arten der NGS-Sequenzierung sind möglich:
- Single-End-Sequenzierung: DNA-Sequenzinformationen werden nur von einem Ende des PCR-Amplikons erhalten. Roche 454, Ion Torrents
- Paarige Endsequenzierung: DNA-Sequenzinformationen werden von beiden Enden des PCR-Amplikons erhalten. Zwei Sequenzen sollten sich um eine ausreichende Länge überlappen, um zu einer einzigen Sequenz zu kombinieren. Illumina
- Circular Consensus Sequencing (cca): Die SMRT-Technologie von Pacific Biosciences bietet sehr lange Einzelmoleküllesungen im Bereich von>10K bp., Aufgrund der verwendeten kreisförmigen Bibliothek kann dasselbe 16S-Amplikon mehrmals sequenziert werden, um eine genaue Konsenssequenz zu erzeugen.